|
Parte 2 - Amplificación por la
PCR
Primera etapa: La Solución "Madre" de PCR
Para preparar la PCR, se agrega Solución
"Madre" de PCR a la muestra de ADN (1) y (2).
Esta solución contiene: agua, un buffer que mantiene la mezcla al pH correcto,
grandes cantidades de los nucleótidos de adenina, timina, citosina y guanina,
grandes cantidades de primers de ADN que "pegan" a la región del ADN
que codifica al gen del ARN ribosómico 16S (para iniciar el proceso de
replicación) y una ADN polimerasa termoestable para catalizar el
alargamiento de la hebra de ADN.
Al mismo tiempo que la muestra se preparan controles positivos y negativos (3). El
control positivo contiene ADN correspondiente a la región del mismo que codifica el ARNr 16S. La
negativa, agua destilada estéril. A ambas se le agrega Solución PCR Madre.
Una vez que los tubos se colocaron en el termociclador ( (4), la "máquina
PCR") comienza el proceso de replicación del ADN.
Segunda etapa: Corriendo la PCR
. Por lo general la
máquina posee un display que indica lo que esta sucediendo.
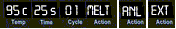
De izquierda a derecha: temperatura, tiempo restante, número del ciclo,
Separación del ADN ("Melt" ), anillado ("ANL")
y alargamiento ("EXT")
El control se configura de la siguiente manera:
Etapa inicial - 10 minutos a 95°C
30 ciclos de las siguientes secuencias de etapas:
-
Separación del ADN (Melt) - 30 segundos a 95°C
-
Anillado (Anneal) - 30 segundos a 60°C
-
Alargamiento (Extend) - 45 segundos a 72°C
Etapa Final de alargamiento - 10 minutes 72°C
Etapa
Final
- 4°C (Conservar a esta temperatura)
Durante cada ciclo, la primera etapa (melt) esta destinada a separar las
hebras de la doble hélice de ADN, (5) y (6) ,por medio del calentamiento a 95°C
durante 30 segundos, del tubo que contiene la mezcla de reacción de la
PCR .
Los primers no pueden pegarse al ADN a esa temperatura, por lo cual el
tubo se enfría a 60°C (7). A esta temperatura los primers se pegan
(anillan..) al ADN monocatenario (8).
La razón por la cual las dos cadenas
de ADN monocatenario no se anillan entre sí, es el gran exceso de primers en
la mezcla, por lo tanto es mucho mas probable que el ADN monocatenario se anille
con un primer que con la otra cadena de ADN.
La etapa final (Extend) consiste en subir la temperatura a
72°C
por
45 segundos lo cual permite a la ADN polimerasa alargar la copia de la hebra de
ADN (9) y (10).
Las tres etapas tardan menos de 2 minutos en producirse y acontecen el el mismo
tubo. Al final de un ciclo se duplica cada pedazo de ADN (11). El ciclo puede
repetirse hasta 30 mas veces, y cada nuevo ADN sintetizado actúa como un nuevo
molde. Luego de 30 ciclos se pueden producir 1.000.000 copias de ADN (12).
16S
ARNr: es un Acido Ribo-Nucléico
asociado con la subunidad pequeña de de los ribosomas de
los procariotas.
Adenina, Citosina, Guanina, Timina: Bases nitrogenadas que conforman el
ADN. A menudo se mencionan únicamente por las letras iniciales A, C, G,
y T. Por su estructura A se aparea con T (dos enlaces puente
hidrógeno) y C con G (tres enlaces puente
hidrógeno), de allí el término de "complementarias" y
esta propiedad es la base de la replicación del ADN.
Anillado (Anneal), Separación (Melt),
Extensión (Extend). En el contexto de la PCR, la fase
de separación (melting) se refiere a la separación de las
hebras del ADN en razón del aumento de temperatura (recuerde que
la unión puente hidrógeno es "débil"). En este
contexto la fase de anillado (annealing) se refiere a la
unión de los primers (que se encuentran en muy altas
concentraciones) a la hebra del ADN monocatenario, al momento de
descender la temperatura del ciclador. La fase de extensión la
ADN polimerasa extiende el extremo 3´ del primer y copia el ADN
correspondiente.
ADN polimerasas: Enzimas que copian una hebra
de ADN que sirve de molde, polimerizando nucleótidos
complementarios con el ADN molde. Las polimerasas extienden la
cadena agregando nucleótidos al extremo 3´ del ADN
"creciente". La polimerización de la cadena de
nucleótidos ocurre uniendo el grupo hidroxilo del carbono 3´ del
azúcar al fosfato del futuro nucleótido adyacente.
BLAST (Basic Local Alignment Search Tool)
conjunto de herramientas informáticas que comparan secuencias de
ADN o proteínas utilizando los datos que se encuentran
disponibles en bases de datos de dominio público. Están
diseñadas para encontrar coincidencias de porciones pequeñas de
ADN o proteínas entre un conjunto de secuencias mayores. BLAST
está disponible en INTERNET su dirección es: http://www.ncbi.nlm.nih.gov/BLAST/
Filogenético (Árbol) : Representación gráfica de de la
historia evolutiva de un organismo representada como un gráfico
ramificado. Estos "árboles" se construyen en base a
diferentes tipos de información. En el caso de las bacterias se
utiliza las similaridades en el ADN para deducir relaciones
entre los mismos, asumiéndose que los mas relacionados comparten
mas similaridades en su ADN que los mas distantes entre sí.
Oligonucleótido:
Una cadena con un pequeño número de nucleótidos.
PCR ("Polymerase Chain Reaction":
La Reacción
en Cadena de la Polimerasa) es una técnica que permite
conseguir muchas copias de ADN . Este procedimientos es uno de los mas
relevantes de la actual revolución en genética molecular. Antes de su
advenimiento, la obtención de grandes cantidades de ADN para su
secuenciación era un proceso largo y tedioso Actualmente la PCR
permite obtener rutinariamente copia copias de ADN provenientes de muestras
muy pequeñas.
En una célula, la doble cadena de ADN es abierta por enzimas para
permitir su replicación.
En la PCR, las hebras simples de
ADN se obtienen calentando fragmentos del mismo a 95°C. La muestra
es luego enfriada para permitir que los "primers"
complementarios se "anillen" a la hebra original de ADN. De esta
manera la ADN polimerasa puede "pegarse" e iniciar la copia de
cada hebra. con calentamientos y enfriamientos repetidos se pueden
producir millones de ADN en unas pocas horas.
El descubrimiento de bacterias extremófilas que soportan temperaturas
alrededor de los 100 ºC permitió aislar sus ADN polimerasas, las cuales
son funcionales a esa temperatura. Las ADN polimerasas aisladas de estas
bacterias permitió el desarrollo de "cicladores" automáticos
que no necesitan que se agregue ADN polimerasa a la muestra luego de cada
ciclo.
Para obtener solamente la porción de ADN necesaria para la
identificación bacteriana se utiliza como "primers"
oligonucleótidos que anillan específicamente a la región que
flanquea al gen del ARN ribosómico 16S .
Primers:
Los "primers" o cebadores son pequeñas piezas de ADN que
anillan a secuencias específicas, en este caso se usan dos primers el 27F
y el 1525R, que se "pegan" a los extremos opuestos del gen del
ARN ribosómico 16S, uno en cada hebra de ADN. Una vez que los
"primers" se anillan la ADN polimerasas extiende e ADN desde el
extremo 5' hasta el 3' final. Los primers se seleccionan en manera tal
que, cuando se forman las dos nuevas copias ellos se superponen ("overlap")
en la región de interés.
Estos "primers" son universales, es decir que anillan ( y por
lo tanto permiten la copia...) del gen del ARN ribosómico 16S de
cualquier bacteria (excepto quizás las mas inusuales). Esto es porque las
secuencias a los cuales se "pega" el primer son extremadamente
similares entre las especies bacterianas (secuencias altamente
conservadas).
Uno se pregunta ¿si son similares como diferencian las especies
bacterianas?. La respuesta es que si bien una parte del gen del ARN
ribosómico 16S es extremadamente similar (secuencias altamente
conservadas) entre diferentes especies, existen otras regiones
extremadamente variables. Los "primers universales" se pegan
a la región altamente conservada del gen, lo cual permite su uso en
una gran variedad de especies bacterianas, pero permiten la copia de las
regiones variables que se usan para la identificación.
Termociclador: Un aparato cuya temperatura puede ser
programada precisamente a una determinada temperatura que se puede
programar para que la cambie rápidamente y de manera cíclica.
Contiene en su interior una gradilla de metal en la cual los tubos
de muestra calzan perfectamente.
|
|
|